L’équipe “(Epi)génomique fonctionnelle métabolique et des dysfonctions dans le diabète de type 2 et des maladies associées” est dirigée par Amélie Bonnefond (amelie.bonnefond@cnrs.fr)
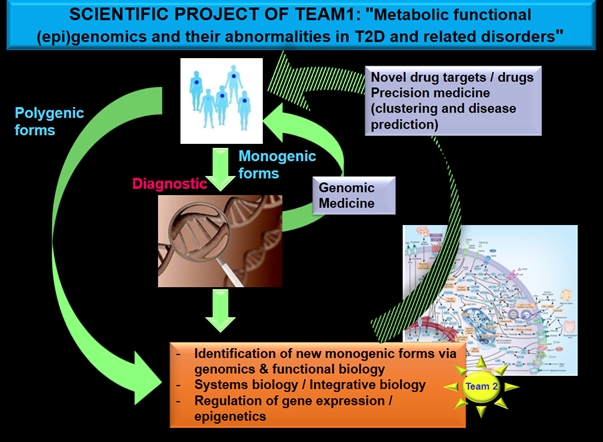
Les projets de l’équipe se focalisent sur les investigations génétiques et génomiques des patients avec une maladie métabolique incluant le diabète de type 2, l’obésité, les dyslipidémies et les maladies rénales.
Chez les patients avec une suspicion de maladie monogénique, nous réalisons un diagnostic moléculaire. Si une mutation pathogène est identifiée dans un gène actionnable, une médecine génomique personnalisée c’est-à-dire spécifique à la cause identifiée est alors directement appliquée. Sinon, nous recherchons de nouvelles étiologies génétiques impliquées via de la génomique et de la biologie fonctionnelle.
Dans les formes complexes polygéniques des maladies métaboliques, nous investiguons des cohortes de patients via des études à grande échelle de biologie des systèmes ou de biologie intégrative utilisant des méthodes holistiques d’exploration du génome, métabolome et bientôt protéome et des analyses bio informatiques et statistiques complexes. En particulier, nous analysons la régulation de l’expression des gènes dans différents tissus et organes. Le but est d’identifier des nouvelles cibles thérapeutiques et de développer des nouveaux traitements. En outre, à travers ces études, nous essayons d’améliorer
1/ la caractérisation des patients de manière à les regrouper en sous-groupes plus homogènes (stratification) afin de progresser vers une médecine de précision, ainsi que
2/ la prédiction des maladies métaboliques dans un objectif de prévention des maladies chroniques.
Ce travail est fait dans le cadre de notre nouveau Centre National de Précision PreciDIAB.
Les axes de recherche de l’équipe sont : (suivez les liens pour plus de détails)